Esta tecnología está basada en la detección de RNA objetivo por medio de la hibridación con oligonucleótidos modificados y su afinidad con anticuerpos acoplados a horse radish peroxidase (HRP). La intención es detectar los niveles de una proteína objetivo a través del RNA templado.
Este es un análisis basado en la afinidad de una hebra de RNA con una hebra complementaria de oligonucleótido detector y oligonucleótido de captura
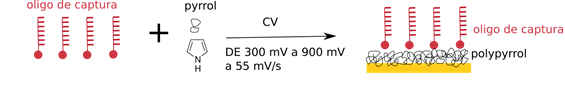
Se inmoviliza un oligonucleótido de captura (rojo) usando pirrol y polimerizándolo a poli-pirrol por medio de voltamperometrías, esto se puede hacer teniendo el primer, una solución de pirrol y un electrodo de oro. Para hacer este procedimiento se usa un POTENSIOSTATO
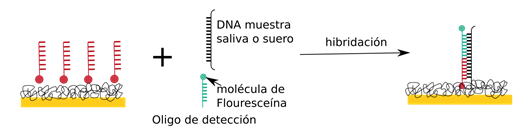
Después se incuban el templado inmovilizado con el oligonucleótido de detección (azul) y el RNA objetivo
El oligonucleótido de detección tiene una molécula de fluoresceína pegada al extremo 3’, si el apareamiento es correcto la fluoresceína puede ser detectada por un anticuerpo específico para fluoresceína que está acoplado a HRP
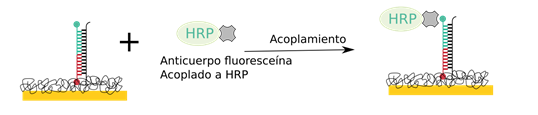
De esta manera tu sistema de detección acoplado está listo y sólo es cuestión de ajustar un potencial en el potensiostato (aplicar un voltaje o potencial). La molécula usada es 3,39,5,59-tetramethylbenzidine (TMB en su estado reducido con H2O2) aplicando en el potensiostato un potencial de -200 mV se generan curvas de detección en función de la reducción de TMB por cronoamperometrías, esta respuesta puede ser calibrada para obtener una línea de calibración corriente vs concentración RNA objetivo.

Para un mejor entendimiento de la metodología EFIRM, es equivalente a un PCR amplificando del cDNA objetivo y enviándolo a secuenciar para corroborar.
[/rt_gal_item][rt_gal_item action=”lightbox” image_id=”10443″]Se añade la muestra y se produce una unión específica en el sensor funcionalizado
[/rt_gal_item][rt_gal_item action=”lightbox” image_id=”10446″]La unión no específica es arrastrada[/rt_gal_item][/rt_image_gallery]

